EEGLABの自動化
STUDYは、ビデオ でEEGLABの特長を紹介しています。
目次
- トピックス
STUDYやBIDSを実装
データのダウンロード https://openneuro.org/datasets/ds003061/ そしてこのフォルダに移動し、次のセクションでスクリプトを実行します。
または、利用可能ないずれかを使用する EEGLAB研究。これらの研究のいくつかは既にそのデータが処理済みであり、自動化された処理には適さないことに注意してください。
ERPの実行
以下のスクリプトを実行すると、ERPパイプラインが実行されます。
EEGLAB では、様々なイベントの開催を予定しています。
% check folder
eeglab;
if ~exist('task-P300_events.json', 'file')
error('Download the data from https://openneuro.org/datasets/ds003061/ and go to the downloaded folder');
else
filepath = fileparts(which('task-P300_events.json'));
end
% import data
pop_editoptions( 'option_storedisk', 1); % only one dataset in memory at a time
[STUDY, ALLEEG] = pop_importbids(filepath, 'studyName','Oddball', 'subjects', [1:2]); % when using all subjects, one subject is truncated and cause the pipeline to return an error
% remove non-ALLEEG channels (it is also possible to process ALLEEG data with non-ALLEEG data
ALLEEG = pop_select( ALLEEG,'rmchannel',{'EXG1','EXG2','EXG3','EXG4','EXG5','EXG6','EXG7','EXG8', 'GSR1', 'GSR2', 'Erg1', 'Erg2', 'Resp', 'Plet', 'Temp'});
% compute average reference
ALLEEG = pop_reref( ALLEEG, []);
% clean data using the clean_rawdata plugin
ALLEEG = pop_clean_rawdata( ALLEEG,'FlatlineCriterion',5,'ChannelCriterion',0.87, ...
'LineNoiseCriterion',4,'Highpass',[0.25 0.75] ,'BurstCriterion',20, ...
'WindowCriterion',0.25,'BurstRejection','on','Distance','Euclidian', ...
'WindowCriterionTolerances',[-Inf 7] ,'fusechanrej',1);
% recompute average reference
ALLEEG = pop_reref( ALLEEG,[]);
% run ICA reducing the dimension by 1 to account for average reference
plugin_askinstall('picard', 'picard', 1); % install Picard plugin
ALLEEG = pop_runica(ALLEEG, 'icatype','picard','concatcond','on','options',{'pca',-1});
% run ICLabel and flag artifactual components
ALLEEG = pop_iclabel(ALLEEG, 'default');
ALLEEG = pop_icflag( ALLEEG,[NaN NaN;0.9 1;0.9 1;NaN NaN;NaN NaN;NaN NaN;NaN NaN]);
% Optional: remove flagged ICA components (otherwise done at the STUDY level), then recompute the
% average reference using the Huber method interpolating missing channels (and removing them again
% after average reference). See tutorial section 5.b.
if 0
ALLEEG = pop_subcomp(ALLEEG, []);
ALLEEG = pop_reref( ALLEEG, [], 'huber', 25, 'interpchan',[], 'refica', 'remove');
end
% extract data epochs
ALLEEG = pop_epoch( ALLEEG,{'oddball_with_reponse','standard'},[-1 2] ,'epochinfo','yes');
ALLEEG = eeg_checkset( ALLEEG );
ALLEEG = pop_rmbase( ALLEEG,[-1000 0] ,[]);
% create STUDY design
STUDY = std_maketrialinfo(STUDY, ALLEEG);
STUDY = std_makedesign(STUDY, ALLEEG, 1, 'name','STUDY.design 1','delfiles','off', ...
'defaultdesign','off','variable1','type','values1',{'oddball_with_reponse','standard'},...
'vartype1','categorical','subjselect', STUDY.subject);
% precompute ERPs at the STUDY level
[STUDY, ALLEEG] = std_precomp(STUDY, ALLEEG, {},'savetrials','on','rmicacomps','on','interp','on','recompute','on','erp','on');
% plot ERPS
STUDY = pop_erpparams(STUDY, 'topotime',350);
chanlocs = eeg_mergelocs(ALLEEG.chanlocs); % get all channels from all datasets
STUDY = std_erpplot(STUDY,ALLEEG,'channels', {chanlocs.labels}, 'design', 1);
% revert default option
pop_editoptions( 'option_storedisk', 0);
pop_importbids() を実行すると、すべての参加者が更新されます。
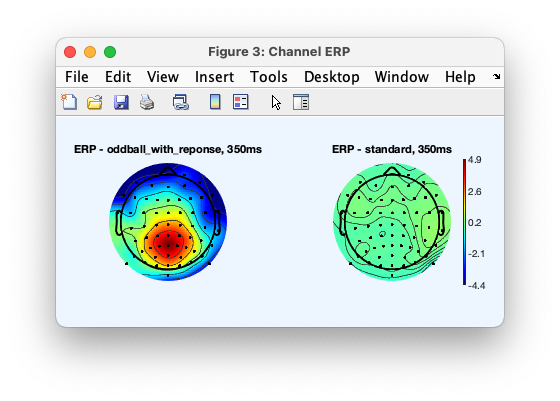
スペクトルパイプラインを実行
以下のスクリプトを実行すると、スペクトルパイプラインが実行されます。エポックデータが必要です。
% check folder
eeglab;
if ~exist('task-P300_events.json', 'file')
error('Download the data from https://openneuro.org/datasets/ds003061/ and go to the downloaded folder');
else
filepath = fileparts(which('task-P300_events.json'));
end
% import data
pop_editoptions( 'option_storedisk', 1); % only one dataset in memory at a time
[STUDY, ALLEEG] = pop_importbids(filepath, 'studyName','Oddball', 'subjects', [1:2]); % when using all subjects, one subject is truncated and cause the pipeline to return an error
% remove non-ALLEEG channels (it is also possible to process ALLEEG data with non-ALLEEG data
ALLEEG = pop_select( ALLEEG,'rmchannel',{'EXG1','EXG2','EXG3','EXG4','EXG5','EXG6','EXG7','EXG8', 'GSR1', 'GSR2', 'Erg1', 'Erg2', 'Resp', 'Plet', 'Temp'});
% compute average reference
ALLEEG = pop_reref( ALLEEG, []);
% clean data using the clean_rawdata plugin
ALLEEG = pop_clean_rawdata( ALLEEG,'FlatlineCriterion',5,'ChannelCriterion',0.87, ...
'LineNoiseCriterion',4,'Highpass',[0.25 0.75] ,'BurstCriterion',20, ...
'WindowCriterion',0.25,'BurstRejection','on','Distance','Euclidian', ...
'WindowCriterionTolerances',[-Inf 7] ,'fusechanrej',1);
% recompute average reference interpolating missing channels (and removing
% them again after average reference - STUDY functions handle them automatically)
ALLEEG = pop_reref( ALLEEG, []);
% run ICA reducing the dimension by 1 to account for average reference
plugin_askinstall('picard', 'picard', 1); % install Picard plugin
ALLEEG = pop_runica(ALLEEG, 'icatype','picard','concatcond','on','options',{'pca',-1});
% run ICLabel and flag artifactual components
ALLEEG = pop_iclabel(ALLEEG, 'default');
ALLEEG = pop_icflag( ALLEEG,[NaN NaN;0.9 1;0.9 1;NaN NaN;NaN NaN;NaN NaN;NaN NaN]);
% Optional: remove flagged ICA components (otherwise done at the STUDY level), then recompute the
% average reference using the Huber method interpolating missing channels (and removing them again
% after average reference). See tutorial section 5.b.
if 0
ALLEEG = pop_subcomp(ALLEEG, []);
ALLEEG = pop_reref( ALLEEG, [], 'huber', 25, 'interpchan',[], 'refica', 'remove');
end
% extract data epochs
% this is not necessary if you have resting state data or eyes open
% eyes closed data, you need to define the design in the STUDY
ALLEEG = pop_epoch( ALLEEG,{'oddball_with_reponse','standard'},[-1 2] ,'epochinfo','yes');
ALLEEG = eeg_checkset( ALLEEG );
% create STUDY design
STUDY = std_maketrialinfo(STUDY, ALLEEG);
STUDY = std_makedesign(STUDY, ALLEEG, 1, 'name','STUDY.design 1','delfiles','off', ...
'defaultdesign','off','variable1','type','values1',{'oddball_with_reponse','standard'},...
'vartype1','categorical','subjselect', STUDY.subject);
% precompute ERPs at the STUDY level
[STUDY, ALLEEG] = std_precomp(STUDY, ALLEEG, {},'savetrials','on','rmicacomps','on','interp','on','recompute','on','spec','on');
% plot ERPS
STUDY = pop_specparams(STUDY, 'topofreq',10);
chanlocs = eeg_mergelocs(ALLEEG.chanlocs); % get all channels from all datasets
STUDY = std_specplot(STUDY,ALLEEG,'channels', {chanlocs.labels}, 'design', 1, 'ylim', [40 55]););
% revert default option
pop_editoptions( 'option_storedisk', 0);
次のようなプロットが表示されます。 上記のアーティファクトを削除するためのオプションが変更されているため、若干異なります。

データのパイプラインの最適化
フィルタリング
clean_rawdata のプラグインは、以下のとおりです。
EEG = pop_eegfiltnew( EEG,'locutoff',0.5);
EEG = clean_artifacts( EEG,'FlatlineCriterion',5,'ChannelCriterion',0.8, ...
'LineNoiseCriterion',4,'Highpass','off' ,'BurstCriterion',20, ...
'WindowCriterion',0.25,'BurstRejection','on','Distance','Euclidian', ...
'WindowCriterionTolerances',[-Inf 7] ,'fusechanrej',1);
clean_rawdata プラグインは、 off と highpass で、 off は、
なぜ2回参照できますか?
clean_rawdata は、よりよく参考にしてください。 2回目の参照は1回目を undoes にします。 こちら.
自動洗浄パラメータ
clean_artifacts は、EEGLAB にあります。 特に、‘ChannelCriterion’ と ‘BurstCriterion’ は別の変数です。 参照 clean_rawdata.
データをクリーニングするための最適なパラメータを見つけることは、パイプラインの設計に不可欠です。 被験者数を実験してみると最高でしょう。 また、すべての被験者に対してパイプラインを実行すると、各被験者に対してどれだけのデータが削除されたかを確認する必要があります。 場合によっては、データの80%は、いくつかの被験者のために削除されます。
より高度なアーティファクト処理の例は、このチュートリアルのセクション を参照してください。
ICAアルゴリズム
EEGLAB のデフォルトは runica (Infomax) です。 論文 を参照。要するに、理想的なアルゴリズムはありません。
- Runica は、Infomaxを使用しています。
- picard は、runica の機能を利用できるようにします。また、ICAの先駆者であるジャン=フランソワ・カルドソが設計しました。
- FastICA はEEGデータで利用可能です。
- Amica は、ベースで動作します。 比較 を参照。EEGデータセットは、
ICLabel
ICLabel では、各コンポーネントの分類を自動的に計算します。 ICLabel を参照してください。
ICAコンポーネントのクラスタリングのダイポール
ICA コンポーネントのクラスタリングの詳細は、STUDY チュートリアルを参照してください。
% find dipoles for all ICA components of all subjects
dipfitPath = fileparts(which('pop_dipfit_settings.m'));
EEG = pop_dipfit_settings( EEG,'hdmfile', fullfile(dipfitPath, 'standard_BEM', 'standard_vol.mat'), ...
'coordformat','MNI','mrifile',fullfile(dipfitPath, 'standard_BEM', 'standard_mri.mat'), ...
'chanfile',fullfile(dipfitPath, 'standard_BEM','elec','standard_1005.elc'), ...
'coord_transform',[-4.8299e-05 1.4553e-05 -0.00010483 2.9747e-06 5.8989e-06 -1.5708 1 1 1] );
EEG = pop_multifit( EEG,[],'threshold',100,'plotopt',{'normlen','on'});
% cluster dipoles which are close to each other and plot one cluster
[STUDY ALLEEG] = std_preclust(STUDY, ALLEEG, 1,{'dipoles','weight',1});
[STUDY] = pop_clust(STUDY, ALLEEG, 'algorithm','Affinity Propagation');
STUDY = std_dipplot(STUDY,ALLEEG,'clusters',2, 'design', 1);
詳しくは、 ICAクラスタリング チュートリアルの。
より高度なパイプライン
参考文献
- プレプ EEGLAB のクリーニングツール。世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界中、世界
- マコトの加工パイプライン
- Danielle Gruberさん EEGLABの使い方。
- BIDSファイル このチュートリアルの一部であり、このページに提示されたものと比較して、同様のパイプライン(より複雑なもの)です。
- EEGLAB論文 EEGLABの概要。
- エポック このプロジェクトでは、EEGLABを使用して分析を提供しています。 神経科学のフロンティア.
- Apiceのこだわり 乳幼児向けデータ
- EEGLABのコンセプト EEG信号のクリーニングのパイプライン管理。
- リラックス ICA と ICLabel は、Windows で自動 EEGLAB のプリプロセスを実装しています。
EEGLAB、FieldTrip、Brainstorm、MNEは、それぞれの強みがあります。各ソフトウェアパッケージの比較は
https://github.com/sccn/eeg_pipelines