ここでは、グループレベルのANOVAを実行するために3つの基本条件を使用します。 LIMOは動く 階層モデル, 被験者レベルのGLM(最初のレベル), グループレベルでのGLM(秒単位). データについていくつかの仮定の下で, これは、ランダムな効果として、すべての被験者のためのすべての試験で混合モデル解析を実行することと等しいです - しかし、はるかに高速に計算します.
第一次レベルの分析
デザイン1の名前をANOVA_Facesに変更し、現在の変数を削除します(図6)。Newをクリックして関心のある変数を追加します。ここではface_typeを選択します(図7)。OKを押して変数を追加し、もう一度OKを押してデザイン選択を閉じます。これでLIMO MEEGデザインを作成し、ERP、スペクトル、またはERSPのモデルパラメータを計算する準備が整います。データ型(ERP、スペクトル、ERSP)を入力し、必要に応じて時間範囲または周波数範囲を制限します。デフォルトのWeighted Least Squares (WLS)は、データフレーム数より試行数が多い限り推奨される方法です。
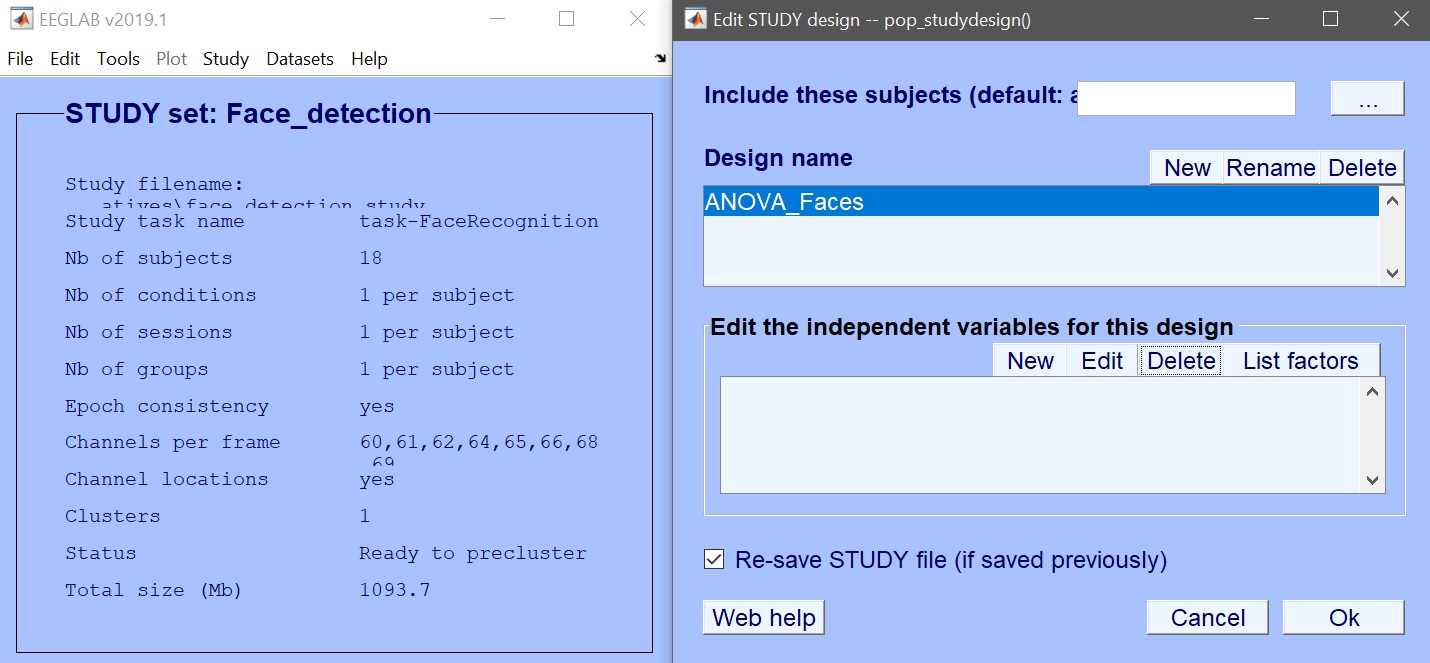 図 6. デザインを編集する
図 6. デザインを編集する
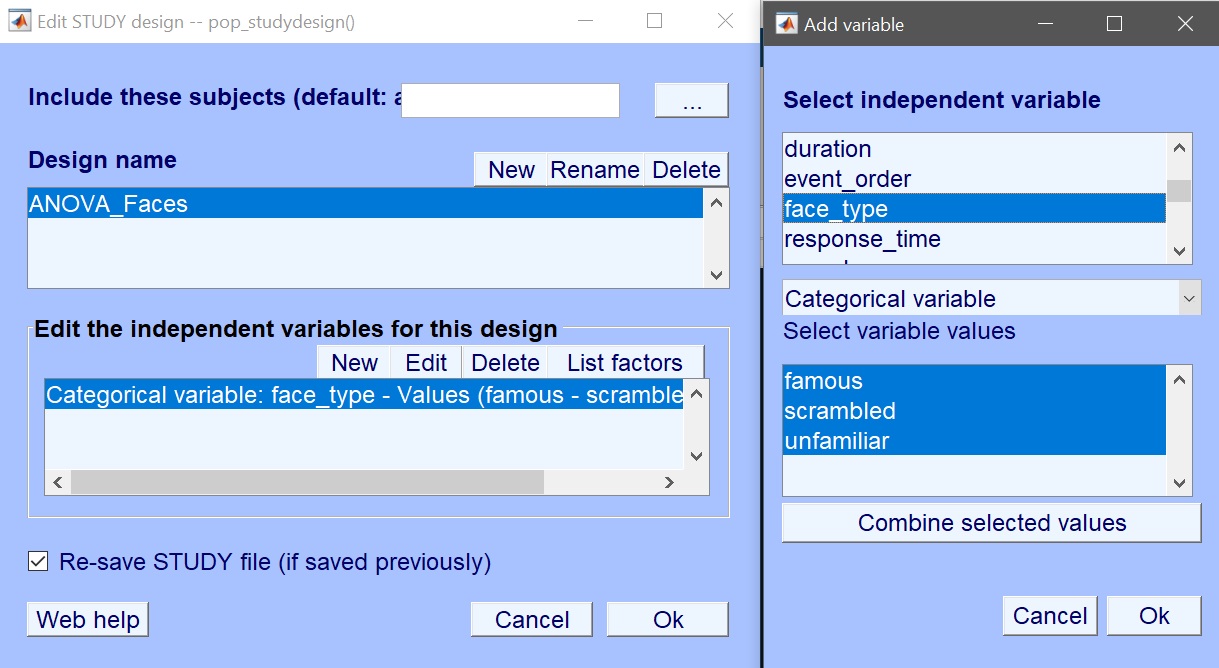 図 7. 新しいデザインを作成する
図 7. 新しいデザインを作成する
これは以下のようにコマンドラインで実行できます。
% 1st level analysis - specify the design
% We ignore the repetition levels using the variable 'face_type'
STUDY = std_makedesign(STUDY, ALLEEG, 1, 'name','ANOVA_Faces','delfiles','off','defaultdesign','off',...
'variable1','face_type','values1',{'famous','scrambled','unfamiliar'},'vartype1','categorical',...
'subjselect',{'sub-002','sub-003','sub-004','sub-005','sub-006','sub-007','sub-008','sub-009',...
'sub-010','sub-011','sub-012','sub-013','sub-014','sub-015','sub-016','sub-017','sub-018','sub-019'});
[STUDY, EEG] = pop_savestudy( STUDY, EEG, 'savemode','resave');
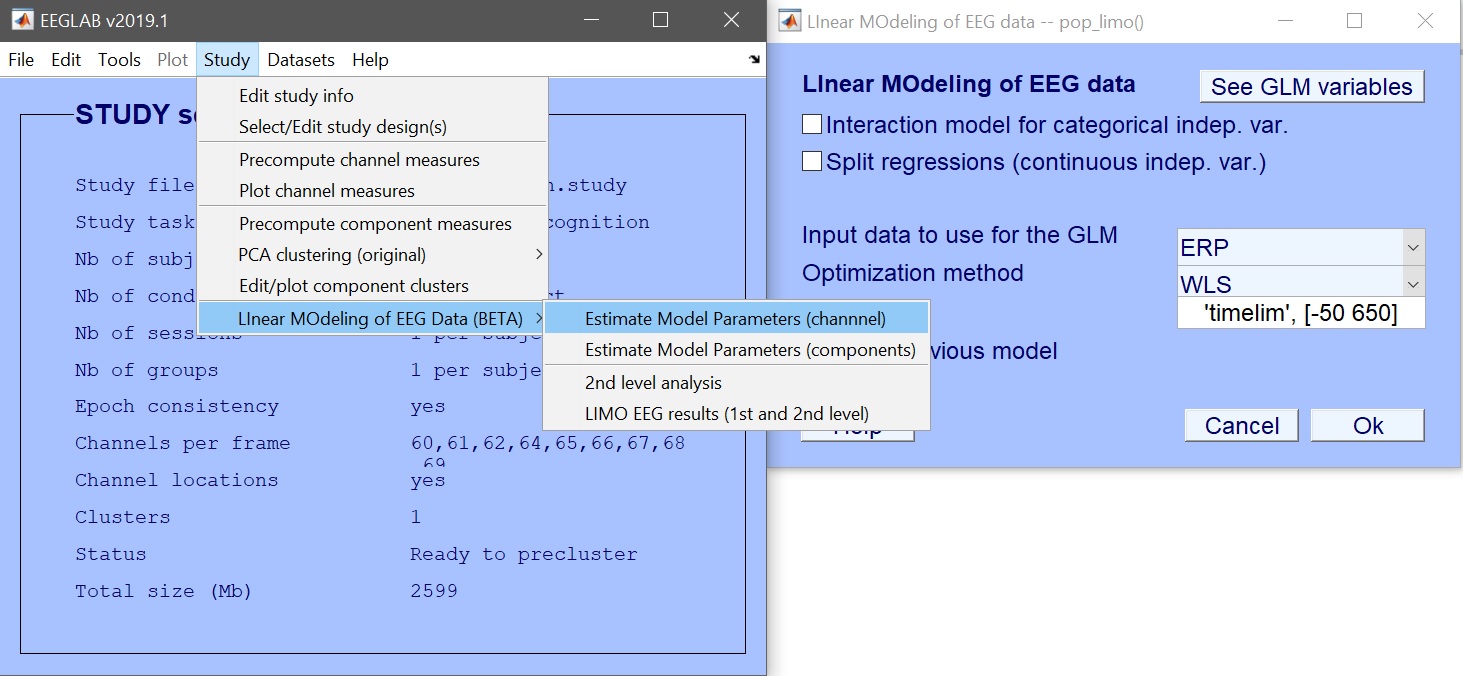
STUDY = pop_limo(STUDY, ALLEEG, 'method','WLS','measure','daterp','timelim',[-50 650],...
'erase','on','splitreg','off','interaction','off');
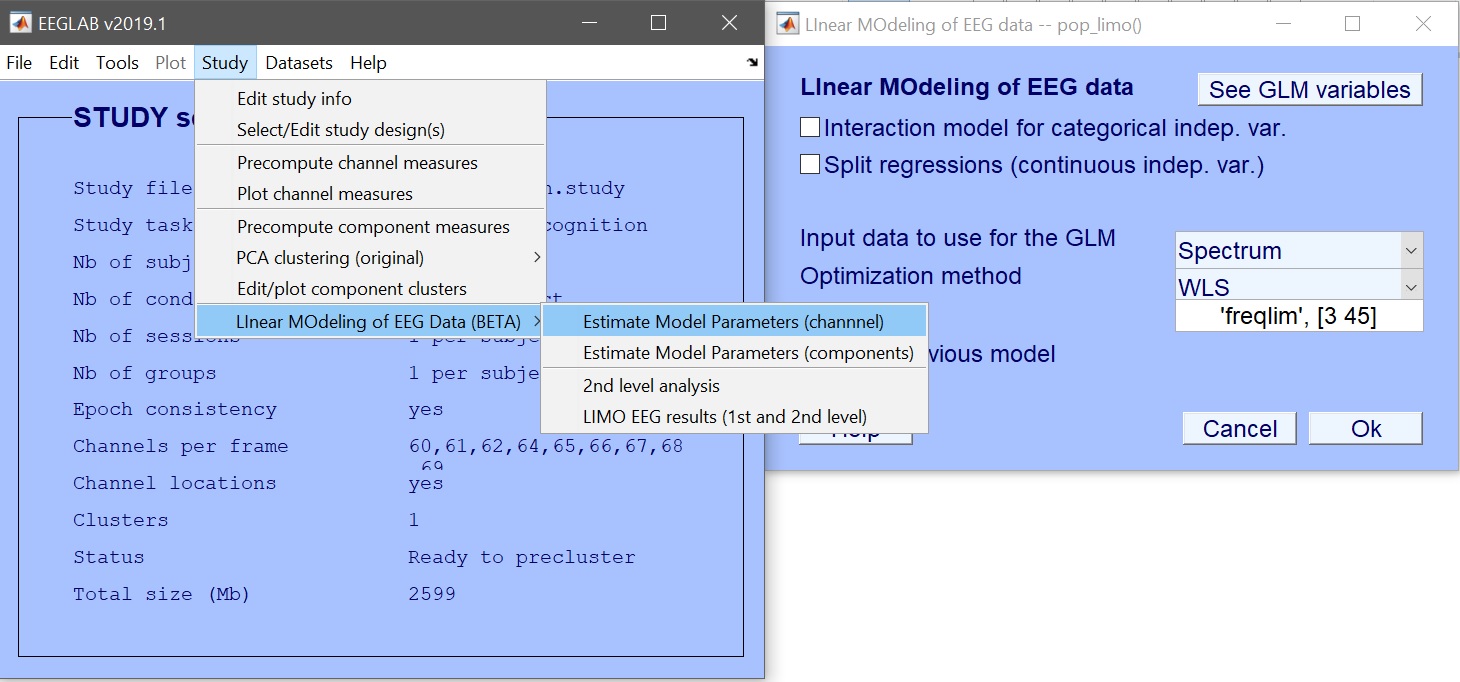
STUDY = pop_limo(STUDY, ALLEEG, 'method','WLS','measure','datspec','freqlim',[3 45],...
'erase','on','splitreg','off','interaction','off');
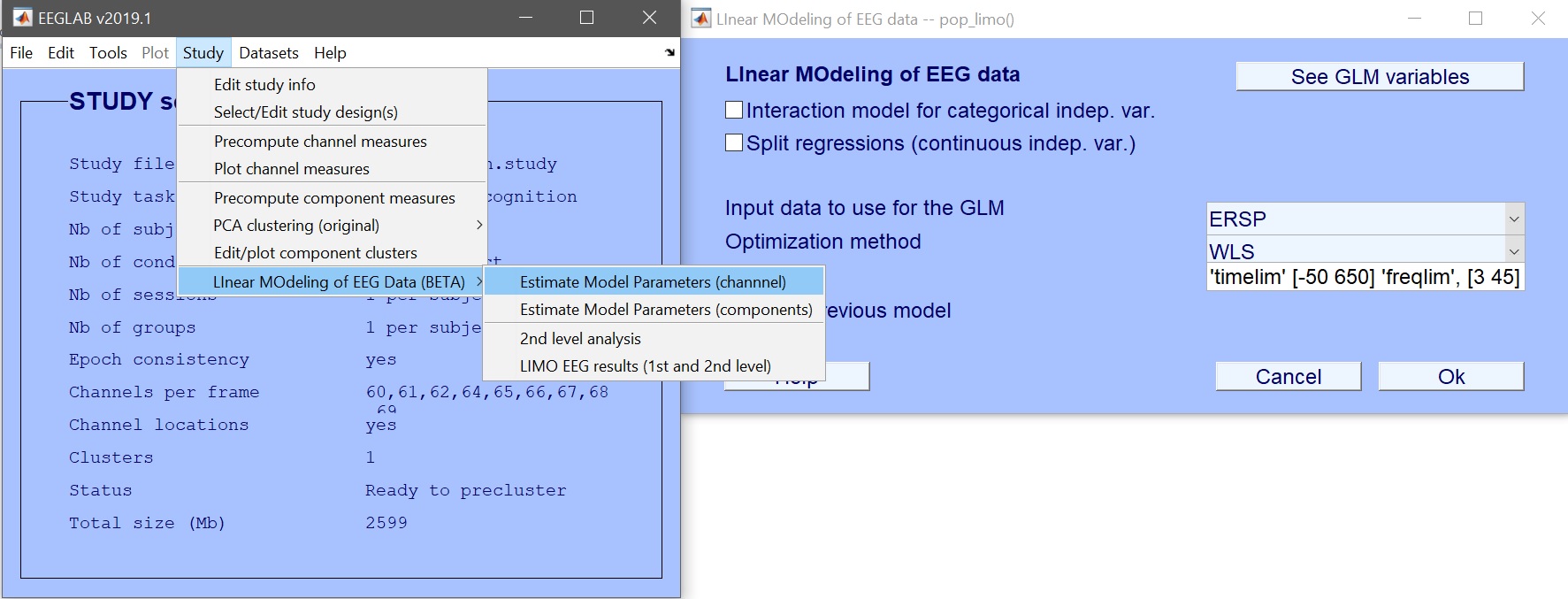
STUDY = pop_limo(STUDY, ALLEEG, 'method','WLS','measure','dattimef',...
'timelim',[-50 650],'freqlim',[3 45],'erase','on','splitreg','off','interaction','off');
図 8. モデルパラメータを推定する_
数分後に、すべての被験者が処理されます。設計は構築され、パラメータが推定されます。 すべての分析は、設計の名前、測定分析、スペース、および使用方法のフォルダ内の各被験者派のフォルダ内に表示されます。 /derivatives/sub-002/eeg/ ANOVA_Faces_GLM_Channels_Time_WLS
インサイドは抽出されたデータ(Yr.mat)、モデル化されたデータ(Yhat.mat)、モデルパラメータ(Betas.mat)、モデル残留物(Res.mat)、モデルフィット(R2.mat)、統計効果(condition_effect_1.mat)、モデル情報自体(LIMO.mat)です。
他のいくつかの便利なファイルもあります。
- LIMO_face_detection は、使用されるすべてのファイルをリストする txt ファイルのフォルダーで、これらはグループレベルの分析に役立ちます
- LIMO_face_detection/limo_batch_report は、 psom のバッチファイルとどのファイルでも失敗したリストを含むフォルダーです。また、psom パイプラインも含まれています。
上記の分析はコマンドラインで以下のように実行できます。
第2レベルの分析
各被験者には、4つのモデルパラメータ(ベータ):馴染みのある、スクランブルされた、非familiar(設計をするときに表示される順序で保存)と最後のパラメータは、対象固有の定数です。 1方向のANOVAは、これらのベータ値(ファイル)を入力するだけで、3つのレベルを持つ単一の要因として設定します。
研究クリック –> EEGデータの線形移動 –> 2ndレベル分析()図9).
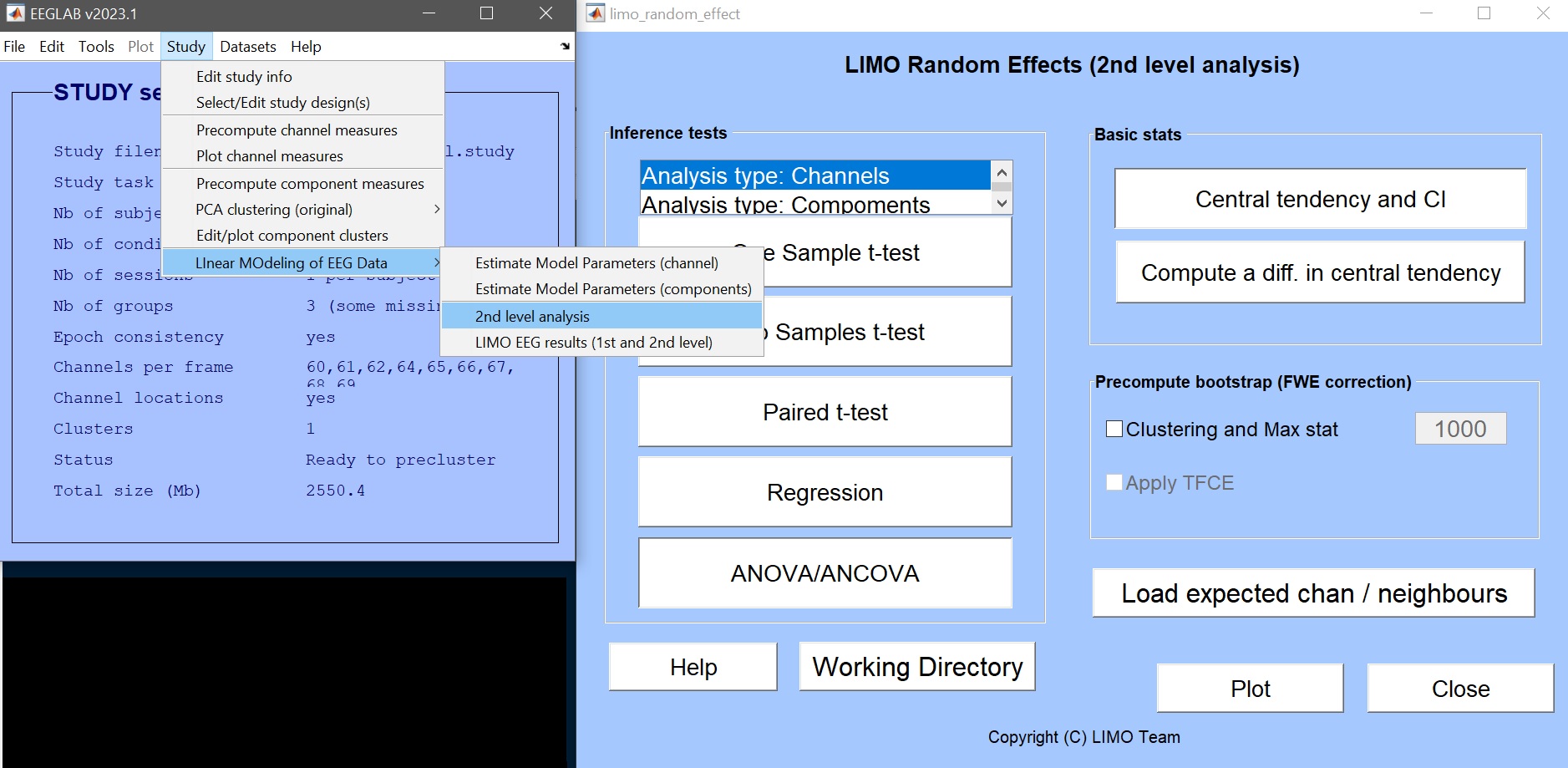 図 9. LIMO第2レベルを呼ぶ_
図 9. LIMO第2レベルを呼ぶ_
- グループレベルのチャンネル位置ファイルをロードします。これは、デリバティブフォルダのルートにあるはずです()図10)
- 新しいディレクトリ(‘1way_ANOVA’)を作り、この新しい解析を保存し、workingディレクトリとして選択します。図11)
- ANOVA/ANCOVA をクリック図12) 必要に応じて情報を記入します。 フルスケール解析 –> 繰り返し測定 ANOVA –> 1 グループ –> 3 レベルの 1 つの要因
- [1 2 3] を分析するベータファイル*を選択し、’faces’ という名前を入力します。図13)
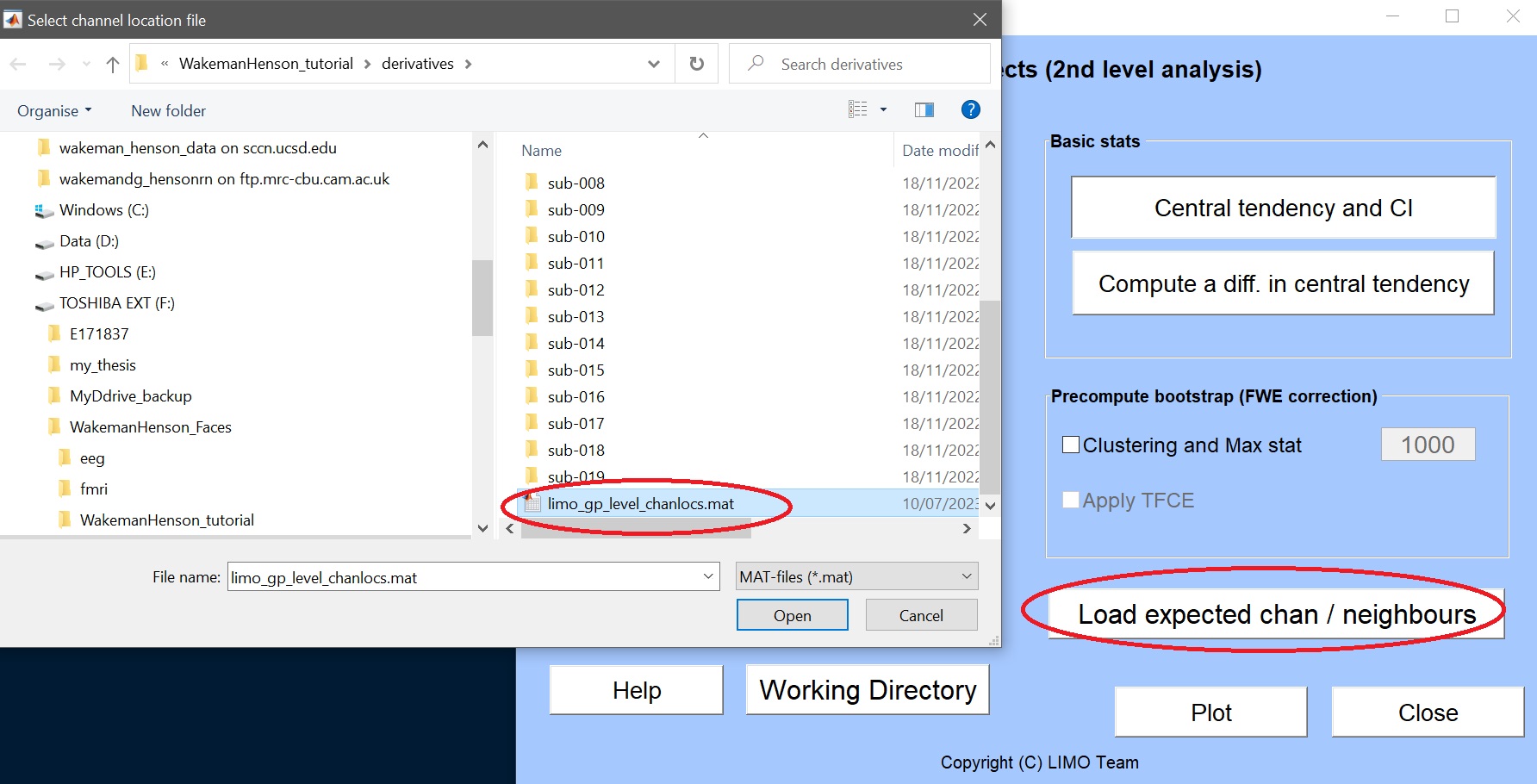 Figure 10. ロードグループ レベルのチャネルの場所 file
Figure 10. ロードグループ レベルのチャネルの場所 file
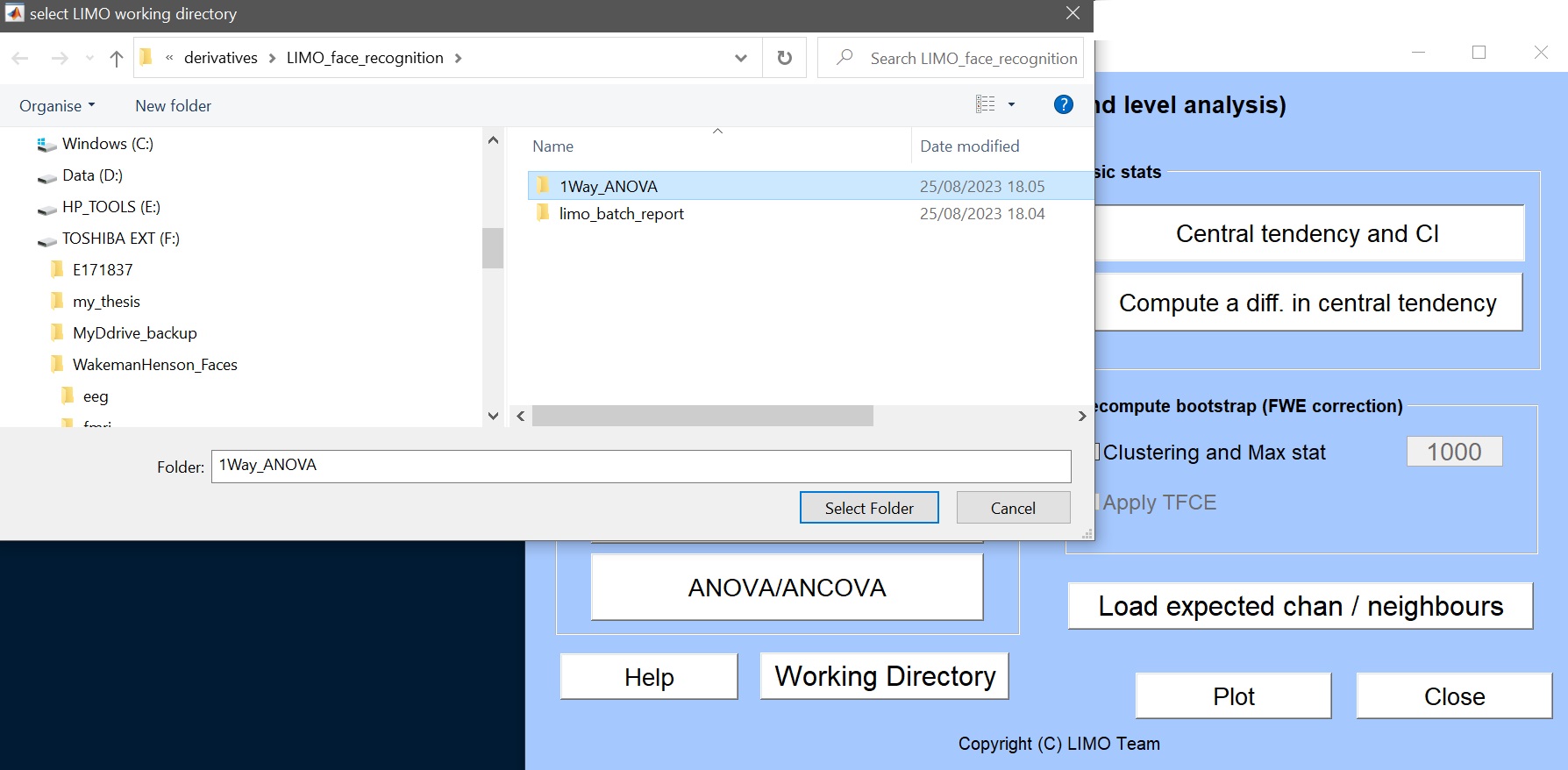 Figure 11. 作業ディレクトリを選択
Figure 11. 作業ディレクトリを選択
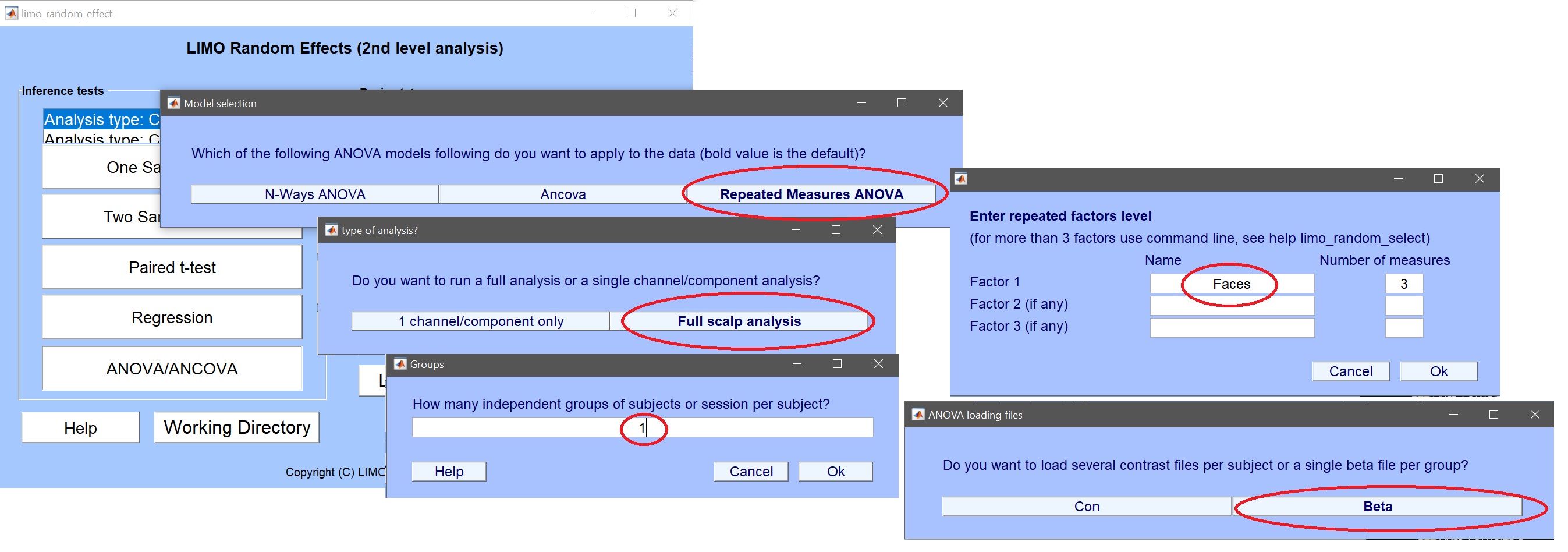 図 12. 1つの方法によって繰り返される測定ANOVA_をセットアップして下さい
図 12. 1つの方法によって繰り返される測定ANOVA_をセットアップして下さい
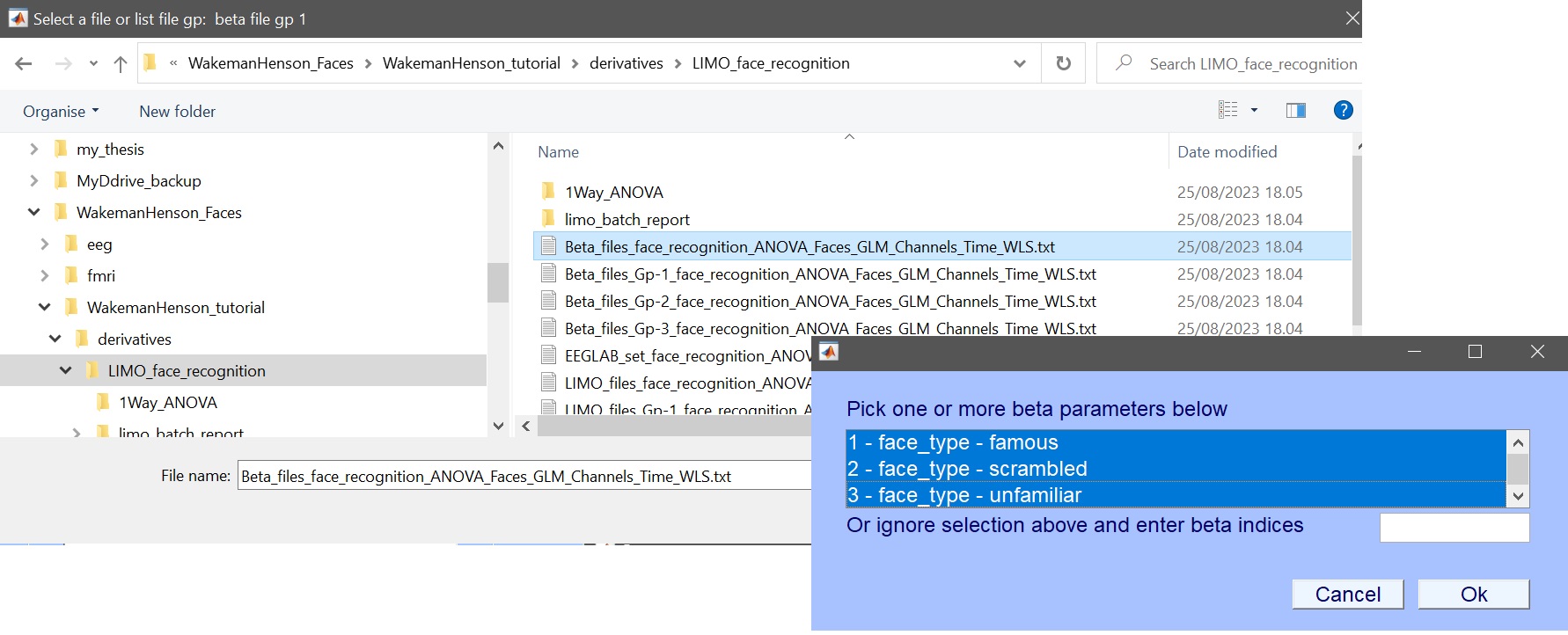 図 13。 ベータファイル(ERP、すなわちチャンネルタイムWLS)とパラメータ_
図 13。 ベータファイル(ERP、すなわちチャンネルタイムWLS)とパラメータ_
設計行列がポップアップする必要があります(図14)、分析を開始するために「はい」に答えます。
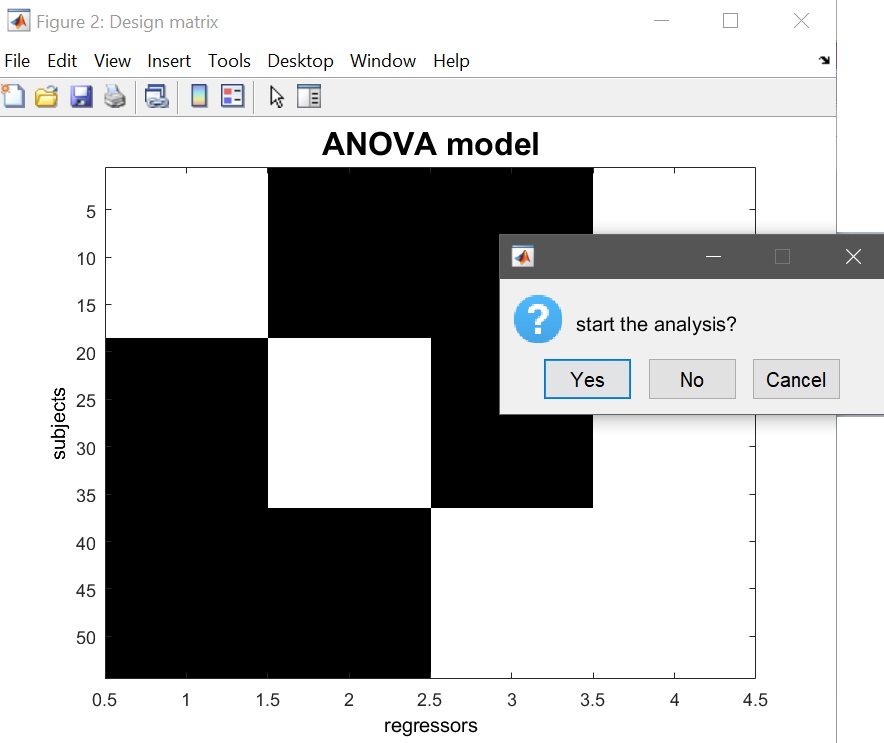 Figure 14. 1ウェイANOVA 設計行列(条件1列+定数)
Figure 14. 1ウェイANOVA 設計行列(条件1列+定数)
これらの手順はコマンドラインで以下のように実行できます。
% 2nd level analysis - ANOVA on Beta parameters 1 2 3
chanlocs = [STUDY.filepath filesep 'limo_gp_level_chanlocs.mat'];
mkdir([STUDY.filepath filesep '1-way-ANOVA'])
cd([STUDY.filepath filesep '1-way-ANOVA'])
% ERP
limo_random_select('Repeated Measures ANOVA',chanlocs,'LIMOfiles',...
{[STUDY.filepath filesep 'LIMO_Face_detection' filesep 'Beta_files_ANOVA_Faces_GLM_Channels_Time_WLS.txt']},...
'analysis_type','Full scalp analysis','parameters',{[1 2 3]},...
'factor names',{'face'},'type','Channels','nboot',1000,'tfce',0,'skip design check','yes');
% Spectrum
limo_random_select('Repeated Measures ANOVA',chanlocs,'LIMOfiles',...
{[STUDY.filepath filesep 'LIMO_Face_detection' filesep 'Beta_files_ANOVA_Faces_GLM_Channels_Frequency_WLS.txt']},...
'analysis_type','Full scalp analysis','parameters',{[1 2 3]},...
'factor names',{'face'},'type','Channels','nboot',1000,'tfce',0,'skip design check','yes');
% ERSP
limo_random_select('Repeated Measures ANOVA',chanlocs,'LIMOfiles',...
{[STUDY.filepath filesep 'LIMO_Face_detection' filesep 'Beta_files_ANOVA_Faces_GLM_Channels_Time-Frequency_WLS.txt']},...
'analysis_type','Full scalp analysis','parameters',{[1 2 3]},...
'factor names',{'face'},'type','Channels','nboot',1000,'tfce',0,'skip design check','yes');
2番目のレベルGUIを終了し、LIMO結果を「プロット」ボタンを押して、ANOVA結果を自動的に提案します。
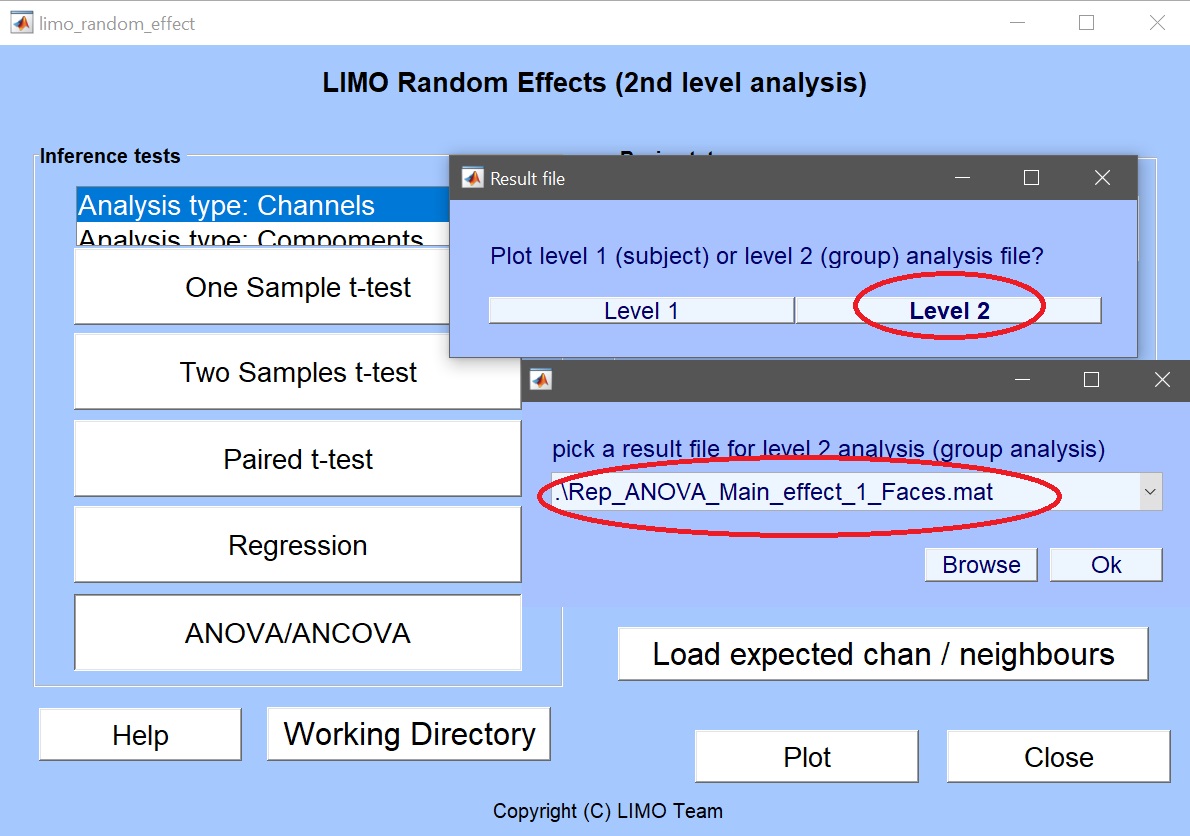
デフォルトでは、bootstrap オプションは’off’ で、ANOVA は素早く計算する必要があります。 ANOVAフォルダ1ウェイでは、データ(Yr.mat)、統計効果(Rep_ANOVA_Main_effect_1_faces.mat)、モデル情報自体(LIMO.mat)が作成されています。
複数の比較方法(例:クラスタリング)を選択し、その後、ブートストラップ(一度だけ行う)を計算します。 数字が更新されるとしばらく経ちます。 新しいH0フォルダには、リサンプリングテーブル(boot_table.mat)、nullデータ(centered_data.mat)、およびH0下にあるブートストラップされた統計結果があります。 コマンドウィンドウで異なるクラスターの結果を報告します。
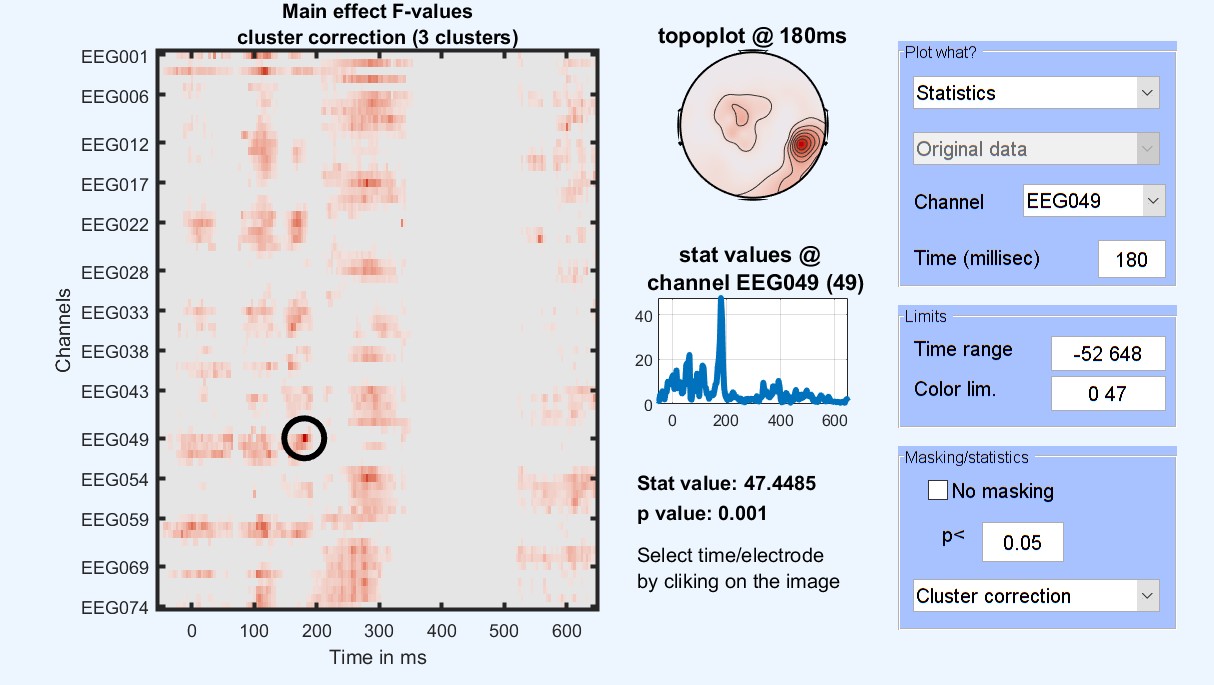
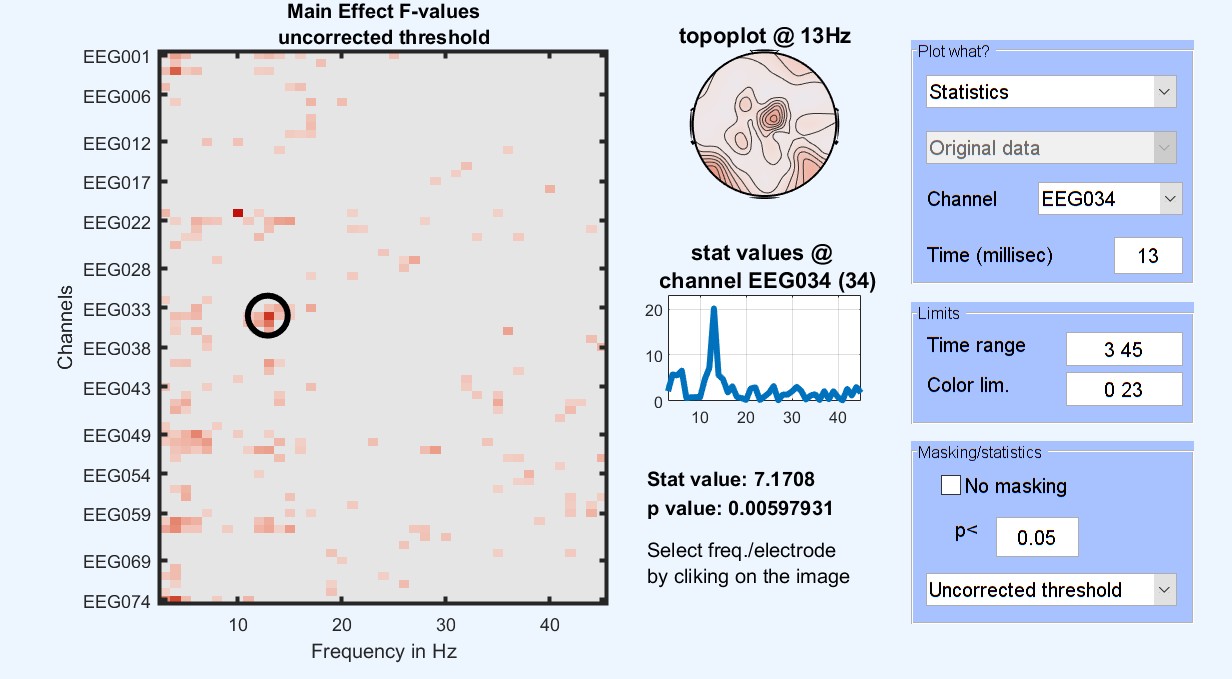
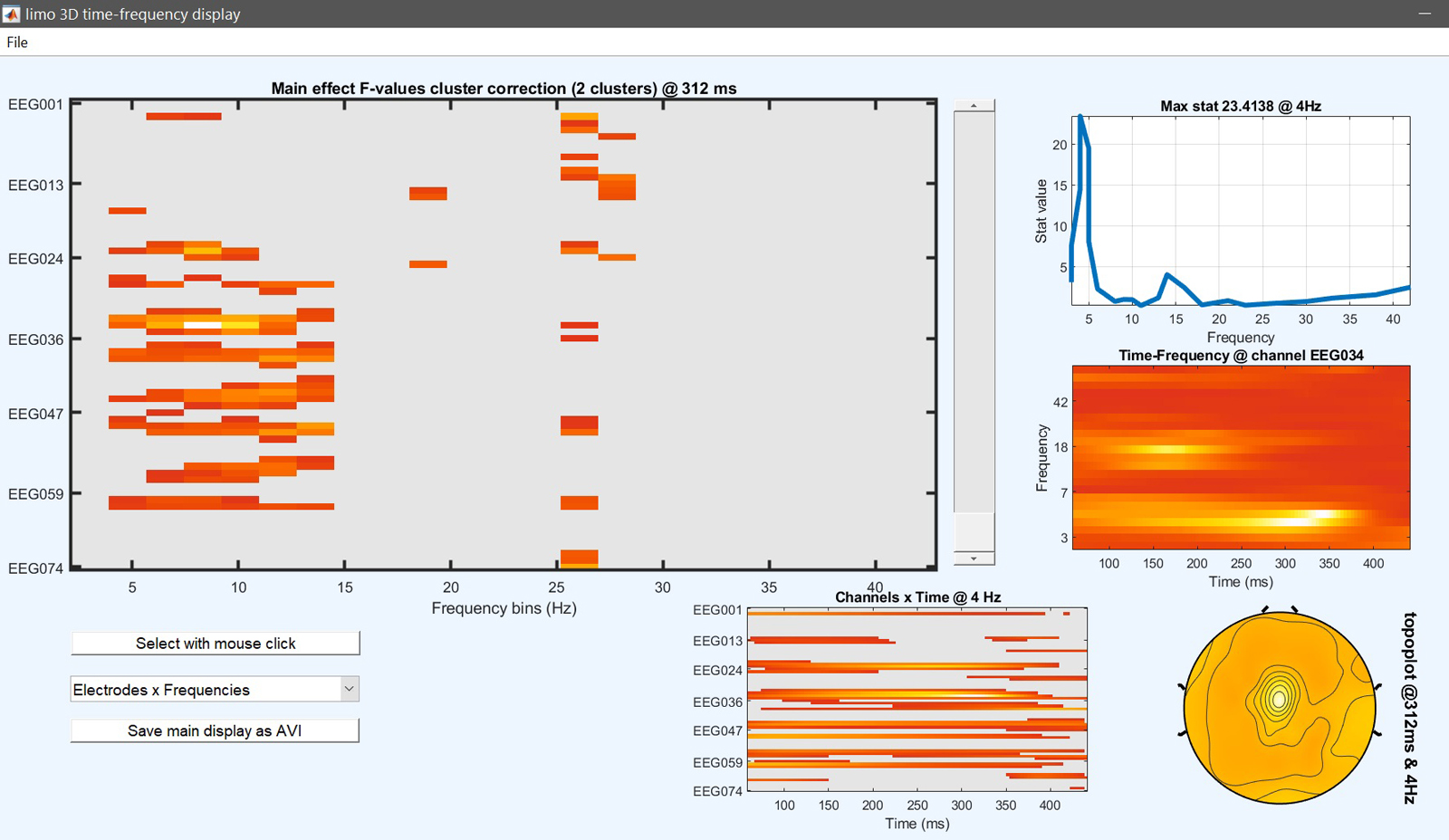 Figure 15. 1ウェイANOVA 有名な顔対スクランブル対比類のない結果
Figure 15. 1ウェイANOVA 有名な顔対スクランブル対比類のない結果
コントラスト
この段階では、ANOVAの結果は、その3つの条件が異なる場所と時刻をお伝えします。 どの条件が他のものと異なるかを確認するには、ポストホックのコントラストは、馴染みのある顔とスクランブルの顔 [1 -1 0] の間のテストを実行することができ、未知は対スクランブル顔 [0 -1 1] と馴染みのある顔対未知面 [1 0 -1]. より複雑なコントラストも考えられます。facesとscrambledの[0.5 -1 0.5]を試してみましょう。これは、顔を含まない画像を含む顔を比較します。 これは、統計ソフトウェアで実行するのと同じ種類のコントラスト/ポストホック分析です。
主要な LIMO MEEG GUI または結果 GUI から、 コントラスト マネージャーをクリックし、 ANOVA 用に作成した「LIMO.mat」ファイルを選択します。 コントラストマネジャーは設計マトリクスを示し、コンピュートのコントラストを入力することができます()図 16) をクリックし、「完了」をクリックします。 コントラストと関連するブートストラップが計算されます。 これらの分析は、主に(i)が繰り返されたANOVAモデル内で計算されているため、(i)、(i)、実行中のアドホックtテストとは異なることに注意してください。つまり、すべての条件と(ii)の会計は、F統計(例えば、ess*ファイルとして保存)に依存する方向性ではありません。
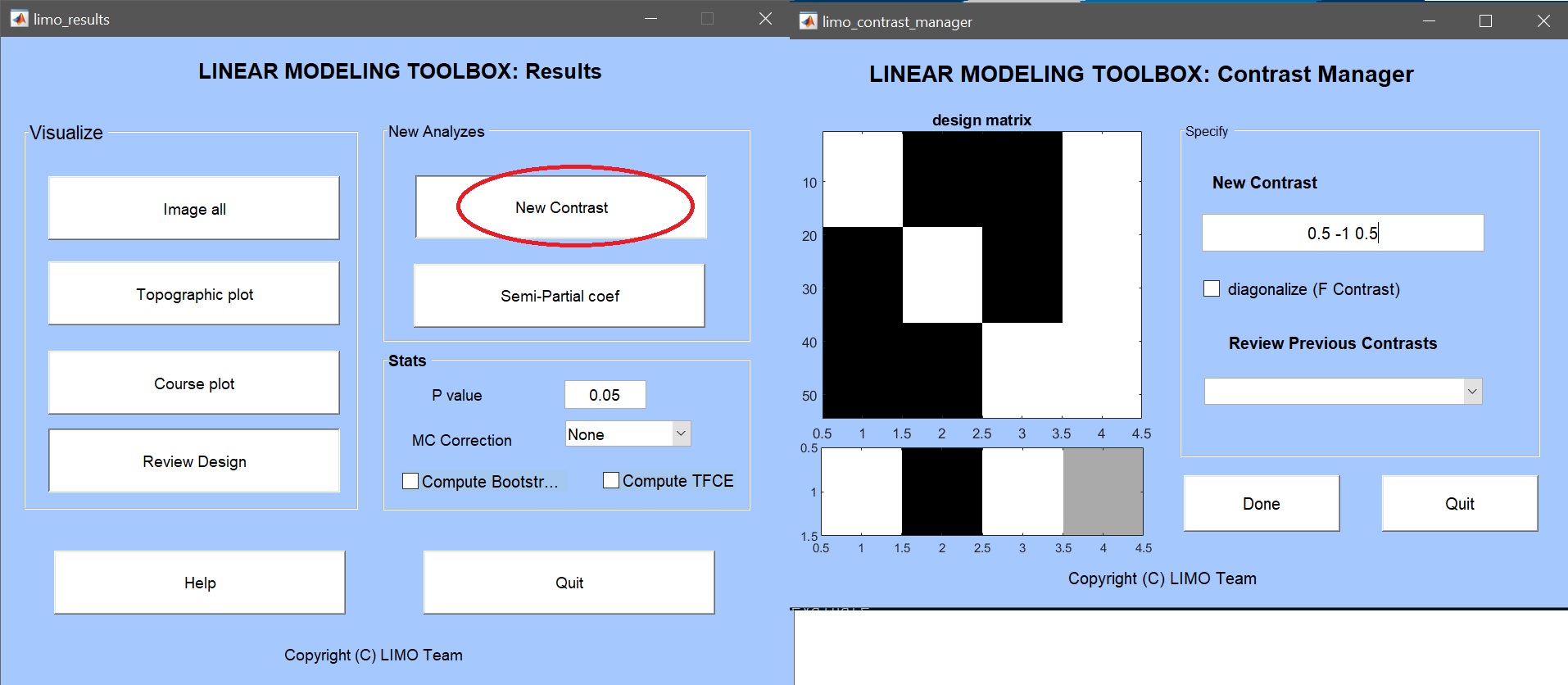 図 16. デザインマトリクス(白)を示すコントラストマネジャー:馴染みのある顔、スクランブルされた顔、非顔、定数)とコントラスト馴染みのある顔 > スクランブル顔。_
図 16. デザインマトリクス(白)を示すコントラストマネジャー:馴染みのある顔、スクランブルされた顔、非顔、定数)とコントラスト馴染みのある顔 > スクランブル顔。_
このステップはコマンドラインで以下のように実行できます。
% add contrast famous+unfamiliar>scrambled
limo_contrast(fullfile(pwd,'Yr.mat'),fullfile(pwd,'LIMO.mat'), 3 ,[0.5 -1 0.5]); % compute a new contrast
limo_contrast(fullfile(pwd,'Yr.mat'),fullfile(pwd,'LIMO.mat'), 4); % do the bootstrap of the last contrast
結果は、新しく作成した「ess*.mat」ファイルを「image all」から選択し、「コースプロット」を使用して、差分時間コース(図17用)を表示することで再び表示できます。 ERP, スペクトラム そして、 ERSP).
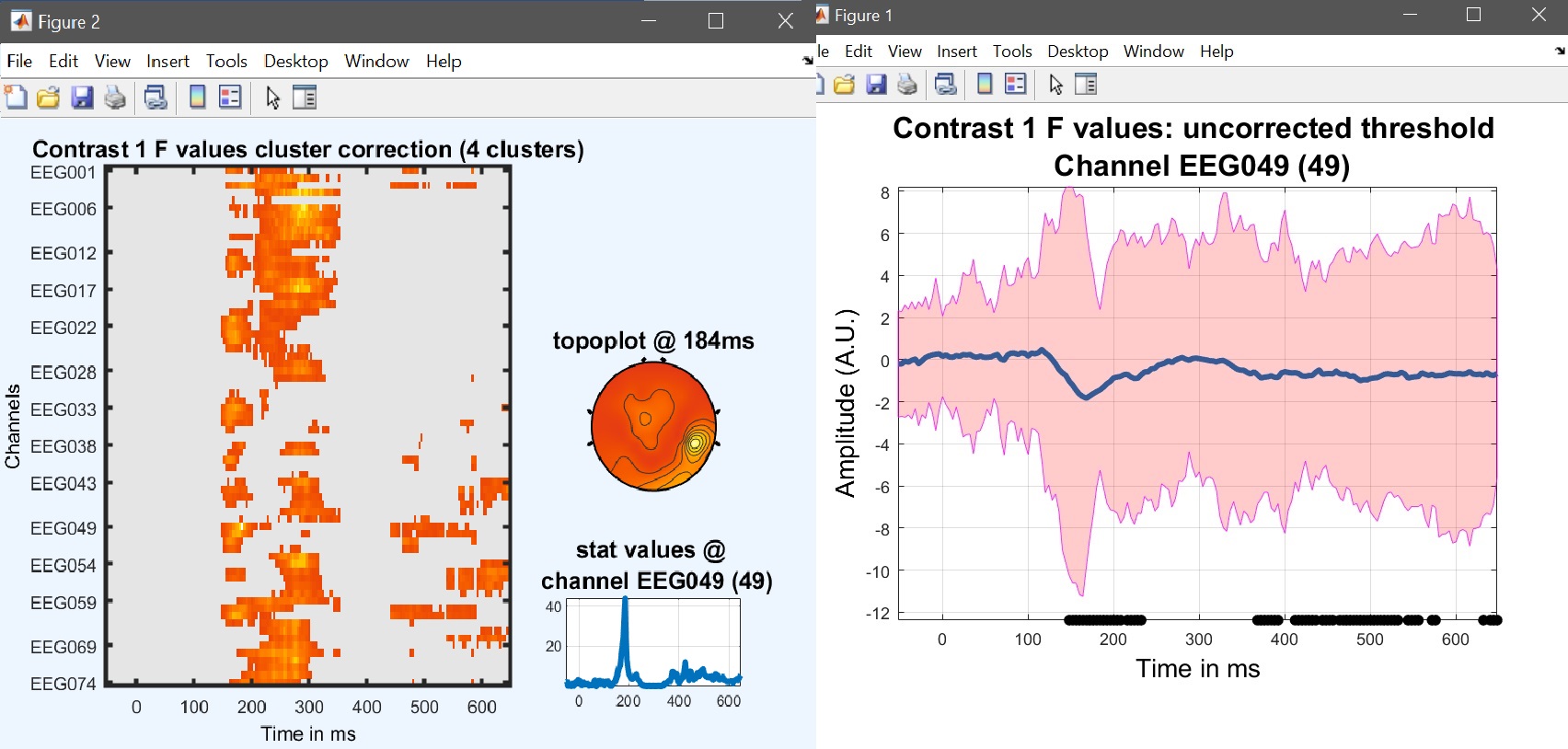
limo_eeg(5,pwd) % channel*time imagesc for both effects and contrast
limo_display_results(3,'ess_1.mat',pwd,0.05,2,fullfile(pwd,'LIMO.mat'),0,'channels',49); % course plot
saveas(gcf, 'contrast_timecourse.fig'); close(gcf)
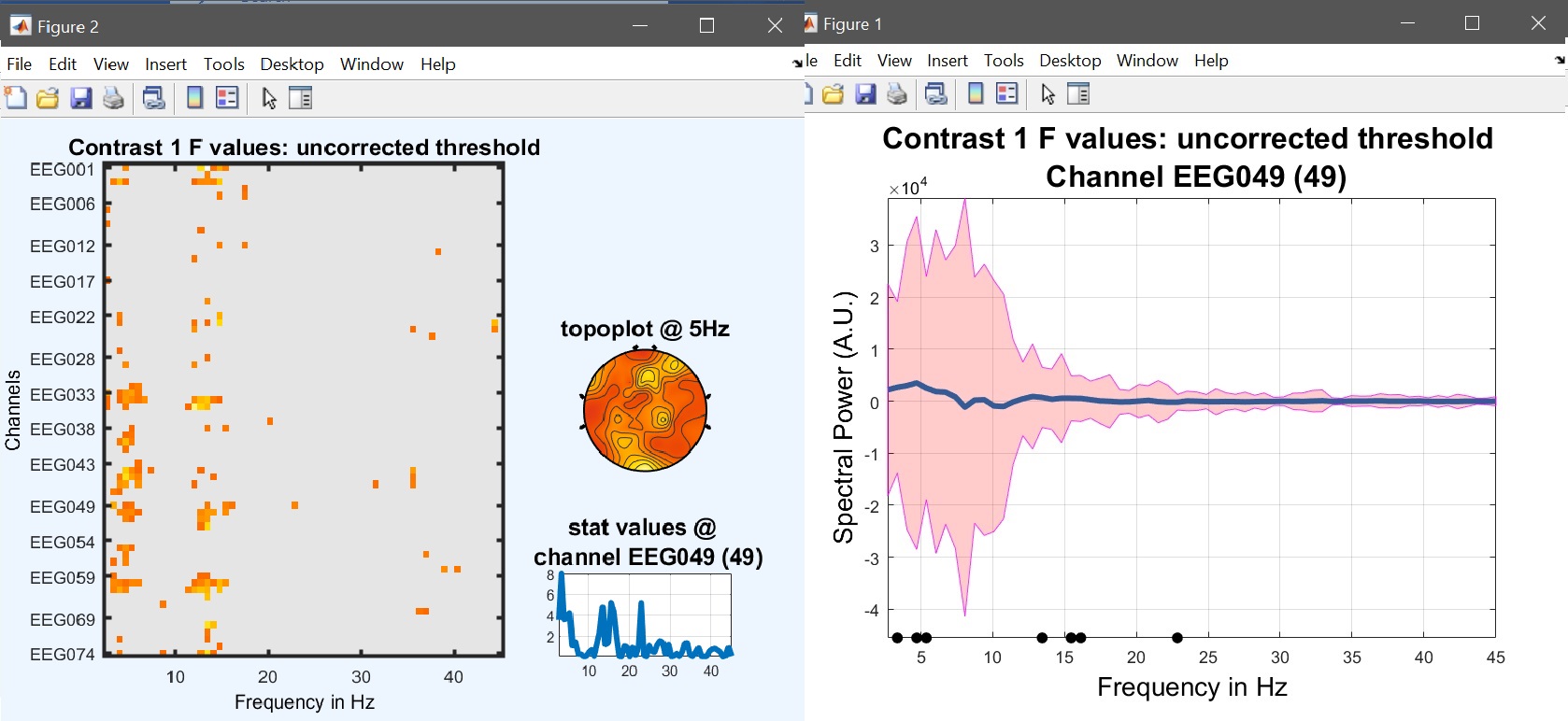
limo_eeg(5,pwd) % channel*time imagesc for both effects and contrast
limo_display_results(3,'ess_1.mat',pwd,0.05,2,fullfile(pwd,'LIMO.mat'),0,'channels',49); % course plot
saveas(gcf, 'contrast_specprofile.fig'); close(gcf)
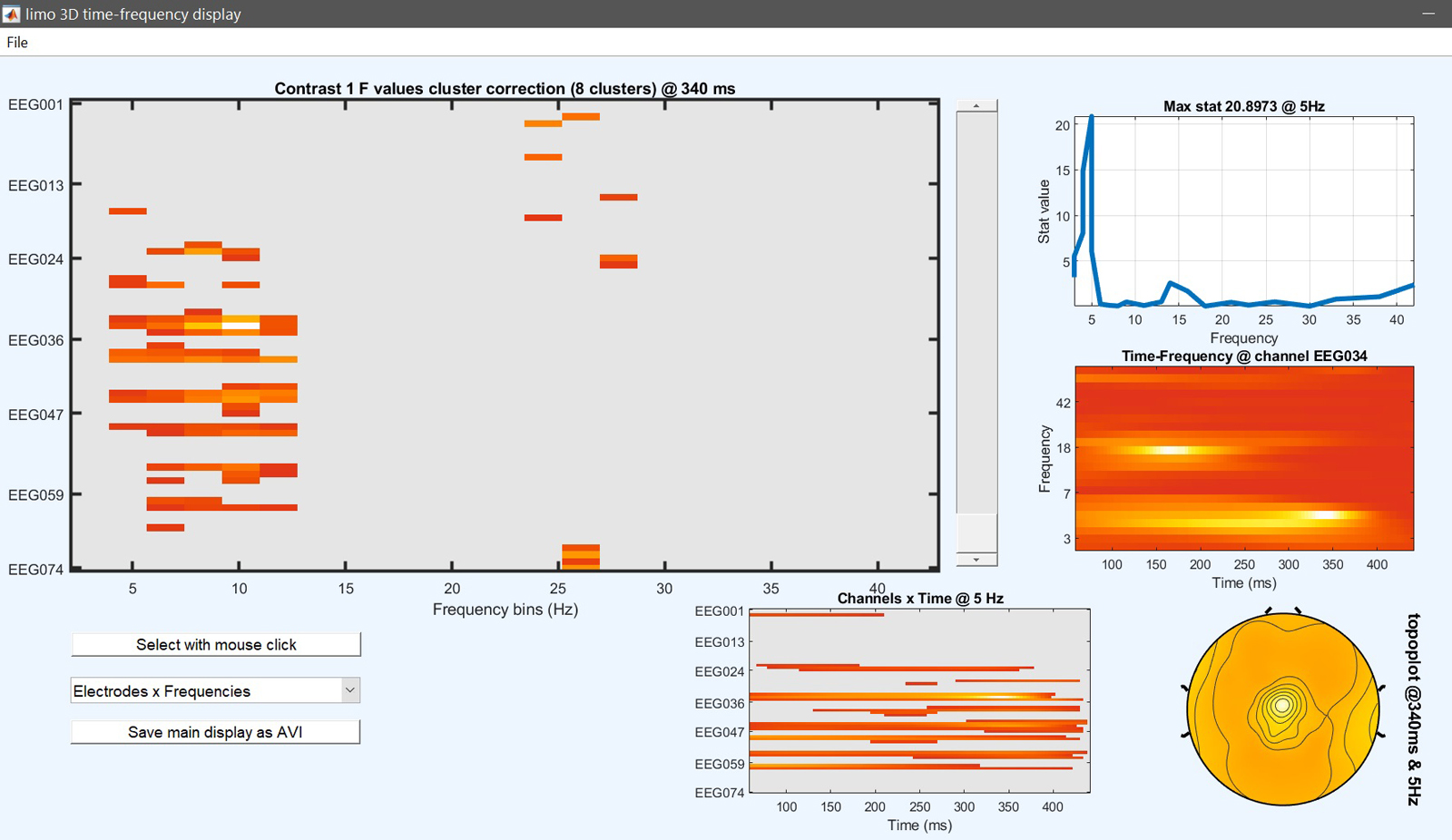
limo_eeg(5,pwd) % channel*time imagesc for both effects and contrast
limo_display_results(3,'ess_1.mat',pwd,0.05,2,fullfile(pwd,'LIMO.mat'),0,'channels',49); % course plot
saveas(gcf, 'contrast_timecourse.fig'); close(gcf)
図 17. コントラストの結果 [0.5 -1 0.5 0] i.e. (顔 - scrambled) 0_